Por

Um estudo inovador que emprega dados completos à escala do genoma revolucionou a nossa compreensão da evolução das aves, revelando novos conhecimentos sobre as relações filogenéticas entre as espécies de aves. Ao analisar um conjunto abrangente de dados de 363 espécies de aves, a pesquisa redefiniu a árvore genealógica das aves, identificando quatro clados principais dentro de Neoaves e lançando luz sobre a complexa história evolutiva das aves. Crédito: SciTechDaily.com
O estudo genómico mais extenso até à data revelou como as aves se espalharam por todo o mundo após a extinção em massa.
Os pássaros representam a única linhagem sobrevivente de dinossauros nos dias atuais. Há cerca de 66 milhões de anos, na transição do Cretáceo Ao período Paleógeno (a fronteira K-Pg), um evento catastrófico de extinção levou ao desaparecimento de todos os dinossauros não-aviários, proporcionando uma oportunidade para as aves se diversificarem rapidamente e ocuparem uma ampla gama de nichos ecológicos.
Neoaves, um grupo diversificado que compreende aproximadamente 95% de todas as aves espécies hoje, emergiu desta radiação. Dos imponentes condores dos Andes aos diminutos beija-flores que voam pelas florestas tropicais, Neoaves abrange uma impressionante diversidade de formas e funções.
Apesar dos esforços consideráveis para reconstruir a história evolutiva das aves e os impactos do evento K-Pg utilizando dados morfológicos e moleculares, a ordem precisa de ramificação e as relações entre as linhagens neoaviárias permaneceram controversas.
“Estudos anteriores em pequenos conjuntos de dados de diferentes regiões genômicas frequentemente produziram resultados conflitantes em relação à topologia da árvore das aves”, disse Guojie Zhang, autor sênior do artigo, professor catedrático de biologia evolutiva na Universidade de Zhejiang e um dos iniciadores do estudo. o projeto B10K. “Neste estudo, pela primeira vez, empregamos dados completos em escala genômica para construir a árvore para espécies de aves de quase todas as famílias representativas.”
Avanços em dados genômicos
Este conjunto completo de dados genômicos foi produzido pelo consórcio B10K em sua segunda fase, que inclui 363 espécies de aves cobrindo todas as principais linhagens de aves.
A nova árvore genealógica está abrindo novos caminhos na longa jornada para desvendar os mistérios da evolução das aves. De acordo com esta árvore genealógica de aves atualizada, um grupo contendo flamingos e mergulhões (chamados Mirandornithes) estava entre as primeiras linhagens neoaviárias a evoluir.
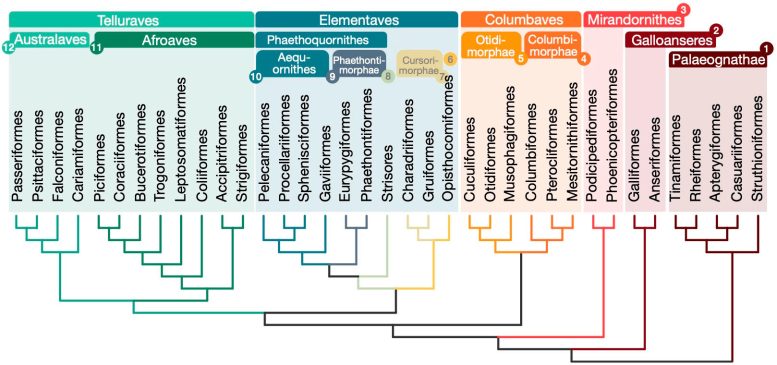
Relações para 363 espécies de aves baseadas em 63.430 loci intergênicos. Crédito: Josefin Stiller
A nova árvore está desafiando a organização dos Neoaves ao classificar este grande grupo em quatro clados principais: Mirandornithes, Columbaves, Elementaves e Telluraves. Elementaves é um agrupamento recentemente proposto compreendendo ca. 14% de todas as espécies de aves modernas, incluindo grupos díspares, como a enigmática cigana, aves limícolas, beija-flores e aves tropicais.
Elementaves foi nomeado para refletir a notável diversidade do grupo em nichos ecológicos, representando os principais elementos da Terra, do ar e da água. Esta nova árvore genealógica resolve alguns debates de longa data sobre as relações entre as espécies de aves e estabelece uma base sólida para o estudo da evolução das aves e do desenvolvimento de características.
O impacto da análise genômica abrangente
Ao empregar dados completos do genoma de 363 espécies de aves, este é o maior conjunto de dados já utilizado para análises filogenéticas de aves. A equipe construiu um novo pipeline para extrair mais de 150 mil regiões espalhadas pelo genoma.
“Caracterizamos as relações filogenéticas em todo o genoma e identificamos padrões associados ao contexto genômico e às características da sequência”, disse Josefin Stiller, principal autora deste estudo e professora assistente em biologia evolutiva na Universidade de Copenhague, “Descobrimos que vários partes do genoma, por exemplo, cromossomos individuais ou genes codificadores de proteínas, muitas vezes sustentam árvores muito diferentes. Isto provavelmente explica porque os estudos que analisaram apenas certas partes genómicas estavam em conflito.”
Reunir grandes quantidades de dados de alta qualidade foi fundamental para produzir uma árvore filogenética robusta. A equipe descobriu que, para a maioria das filiais, é possível chegar a um consenso sobre seus relacionamentos quando uma quantidade suficiente de dados é usada. Mas as posições filogenéticas de alguns grupos de aves, como corujas e falcões, permanecem intrigantes, mesmo com dados em escala completa do genoma.
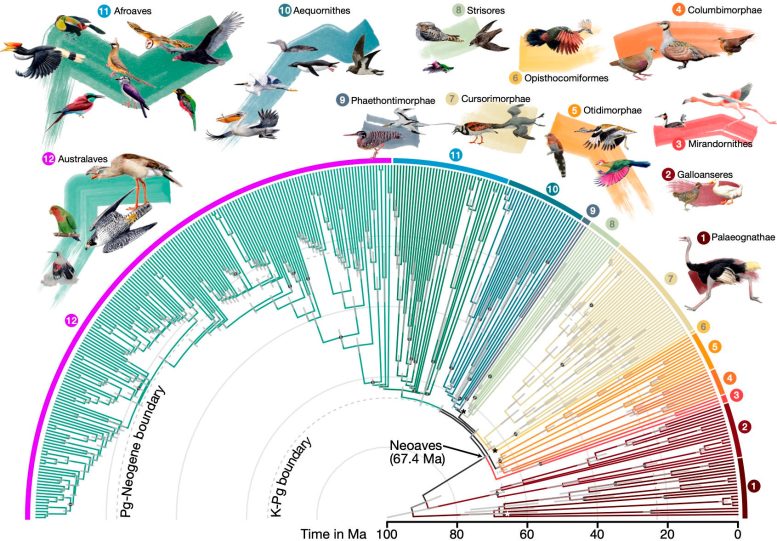
Tempos de divergência para 363 espécies de aves com base em 63.430 loci intergênicos. Crédito: Josefin Stiller
“Mais dados não produzem necessariamente uma solução melhor”, disse Zhang. Siavash Mirarab, co-autor sênior do estudo, professor de engenharia elétrica e de computação na Universidade da Califórnia, San Diego, acrescentou que: “A razão para isso pode ser alguma história evolutiva complexa, como o antigo acasalamento cruzado entre duas linhagens, classificação de linhagem incompleta, atração de ramos longos e parcialidade ADN conteúdo de sequência, o que pode interferir na reconstrução de árvores filogenéticas.”
O estudo relata novos insights sobre quais desses fatores impactam quais ramos da árvore, fornecendo uma imagem mais abrangente e genuína da origem desses grupos de aves. O estudo também propõe uma escala de tempo mais precisa para a diversificação das aves modernas, sugerindo que uma rápida radiação ocorreu durante ou perto da extinção em massa na fronteira Cretáceo-Paleógeno (K-Pg) e em menor grau logo após o Paleógeno-Neógeno. limite.
Os pesquisadores descobriram que essas radiações coincidiam com mudanças genéticas e morfológicas notáveis entre as aves, incluindo maiores taxas de mutação, tamanhos corporais menores, cérebros maiores e tamanhos populacionais efetivos maiores. “Isto ilustra o poder da genómica comparativa: ao comparar genomas de espécies vivas, podemos descobrir vestígios de eventos que aconteceram há 66 milhões de anos”, disse Stiller.
“Nosso trabalho mudou muitas visões tradicionais sobre a história evolutiva das aves. Esta nova árvore genealógica servirá como uma base sólida para mapear a história evolutiva de todas as espécies de aves, com implicações importantes para a investigação ornitológica e estudos de biodiversidade”, concluiu Zhang.
Referência: “Complexidade da evolução aviária revelada pelos genomas de nível familiar” por Josephine Stiller, Shaohong Feng, Al-Aabid Chowdhury, Iker Rivas-Gonzalez, David A. Duchene, Qi Fang, Yuan Deng, Alexey Kozlov, Alexandros Stamatakis, James Claramunt , Jacqueline MT Nguyen , Simon YW Ho , Brant C. Faircloth , Julia Haag , Peter Houde , Joel Cracraft , Metin Balaban , Uyen Mai , Guangji Chen , Rongsheng Gao , Chengran Zhou , Yulong Xie , Zijian Huang , Zhen Cao , Zhi Yan , Huw A. Ogilvie, Luay Nakhleh, Bent Lindow, Benoit Morel, Jon Fjeldsø, Peter A. Hosner, Rute R. da Fonseca, Bent Petersen, Joseph A. Tobias, Tamas Szekely, Jonathan David Kennedy, Andrew Hart Reeve, Andras Liker, Martin Starvander, Agostinho Antunes, Dieter Thomas Tietze, Mads Bertelsen, Fumin Lei, Carsten Rahbek, Gary R. Graves, Mikkel H. Schierup, Tandy Warnow, Edward L. Braun, M. Thomas P. Gilbert, Erich D. Jarvis, Siavash Mirarab e Guojie Zhang, 1º de abril de 2024, Natureza.
DOI: 10.1038/s41586-024-07323-1